اهمیت بررسی و پیشبینی ساختار سه بعدی پروتئین ها
بررسی و شناسایی ساختار 3بعدی پروتئین ها یک منبع بسیارمهم از اطلاعات برای درک عملکرد و فعالیت پروتئین ها ، میانکنش آنها با لیگاندها ، پروتئین ، DNA و … همچنین درک اثرات جهش ها میباشد.
آموزش روش های پیش بینی ساختار سه بعدی پروتئین ها
ساختار سه بعدی پروتئین بر اساس سه روش اصلی طبقه بندی شود :
توضیح روش مدل سازی همولوژیکی برای پیش بینی ساختار سه بعدی پروتئین ها
روش مدل سازی همولوژیکی: در این روش اساس پیشبینی ساختار سه بعدی پروتئین ها توسط مدل سازی همولوژیکی ای می باشد که در آن توالی پروتئین با یک یا تعداد بیشتری از پروتئین ها که ساختار آن ها از قبل شناخته شده و دارای شباهت هستند، می باشد. اساس این روش که مدل سازی مقایسه ای نیز نامیده می شود این است که که پروتئینهایی با توالی ها ی مشابه دارای ساختارهای مشابه نیز می باشند . زیرا وقتی ساختار یک پروتئین از یک خانواده ژنی بهوسیلهی آزمایش تعیین می گردد، پروتئین های دیگر آن خانواده نیز میتوانند بر اساس شباهتشان با ساختار پروتئین شناخته شده، مدل سازی شوند. در این روش دقت پیش گویی به میزان تشابه بین توالی پروتئین هدف و پروتئین الگو بستگی دارد. مشکل اصلی پیش بینی ساختار سوم پروتئین ها با روش مدل سازی همولوژیکی در یافتن توالی هدفی است که به عنوان الگو استفاده می گردد و تقریبا 57 درصد همهی توالی های شناخته شده حداقل یک دمین دارند که به یک پروتئین با ساختار شناخته شده وابسته میباشد.
توضیح روش مدل سازی AB initio برای پیش بینی ساختار سه بعدی پروتئین ها
در روش AB initio سعی می شود تا مدل ساختار سهبعدی پروتئین ها با استفاده از توالی و بررسی و پیش بینی نیروهای بیم اتم های پروتئین ها ایجاد گردد. و از اطلاعات ساختار سه بعدی موجود استفاده نمی شود. این روش همچنین روش دنوو نیز نامیده می شود.
با این که این روش از لحاظ کامپیوتری بسیار پیچیده و فاقد دقت کافی می باشد اما به چند ازا ین روش استفاده میشود و در حال گسترش میباشند. اول این که در برخی از موارد حتی یک ساختار همولوگ وابسته خیلی دورهم ممکن است در دسترس نباشد. در این موارد ab initio تنها روش پیش بینی ساختار سه بعدی پروتئین مربوطه میباشد . دلیل دوم این است که ممکن است ساختارهای جدیدی شناسایی شوند که بهوسیلهی روشهایی که اساس شان مقایسهی ساختارهای شناخته شده است قابل شناسایی نباشند.
توضیح روش مدل سازی threading پروتئین برای پیش بینی ساختار سه بعدی پروتئین ها
این روش که گاهی نیز تشخیص فولد پروتئین نامیده می شود یک رویکرد حد واسط دو روش قبلی می باشد که هم از تشابه همولوژی توالی (البته در صورت وجود) و هم از اطلاعات مربوط به تطابقهای ساختاری استفاده می نماید. در این روش هدف تطابق توالی پروتئین هدف با ساختار شناخته شده در کتابخانهای از فولد ها میباشد.
آموزش پیش بینی ساختار سه بعدی پروتئین ها با روش swissmodel
در ادامه آموزش سایت swissmodel برای پیشبینی ساختار سهبعدی پروتئینها بر اساس روش مدل سازی همولوژیکی ارائه میگردد.
در این روش پیشبینی ساختار سهبعدی پروتئین بر اساس توالی پروتئین صورت میپذیرد. پیشبینی ساختار سهبعدی پروتئین در سایت swissmodel با دو روش امکانپذیر است
- در روش اول سایت swissmodel به صورت خودکار الگوهای لازم برای پیشبینی ساختار سهبعدی پروتئین را تعیین مینماید
- در روش دوم باید فایل الگو برای پیشبینی ساختار سهبعدی پروتئین را در سایت swissmodel وارد نماییم.
روش اول برای پیشبینی ساختار سهبعدی پروتئین در سایت swissmodel
ابتدا بر روی لینک زیر کلیک نمایید تا به سایت وارد شوید
https://swissmodel.expasy.org/interactive
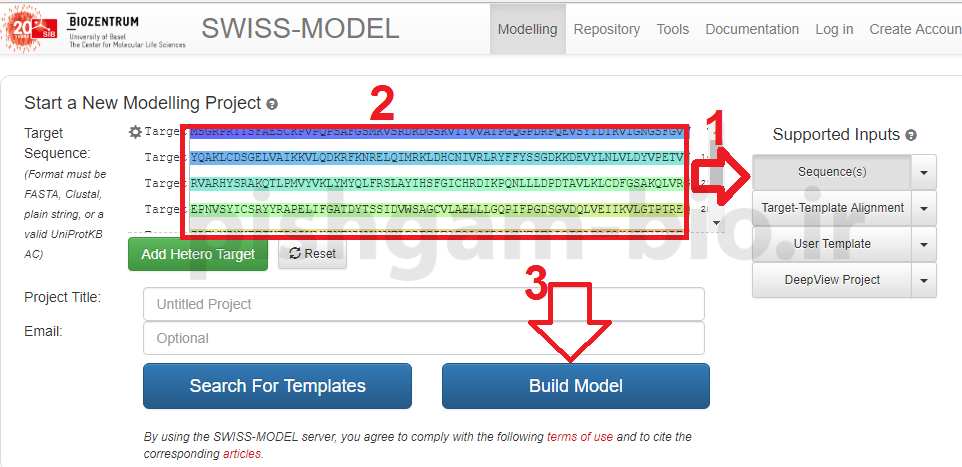
در صفحه اصلی سایت:
1:از بین گزینهها مختلف بر روی Sequence کلیک نمایید
2: توالی پروتئین را وارد نمایید3: بر روی Build Model کلیک نمایید تا فرایند پیشبینی ساختار سهبعدی پروتئین آغاز شود.
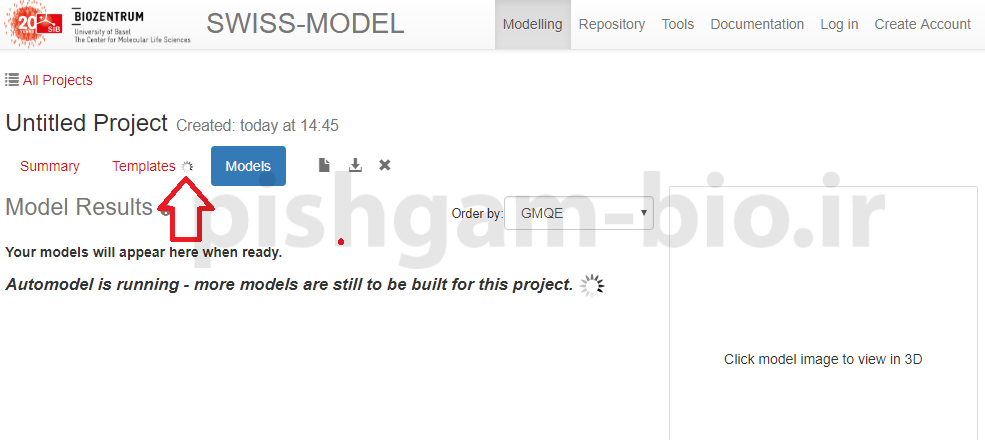
ابتدا نرم افزار به جستجوی الگوی ها مناسب برای پیشبینی ساختار سهبعدی میپردازد و بعد از این مرحله ساختار سهبعدی را پیشبینی مینماید
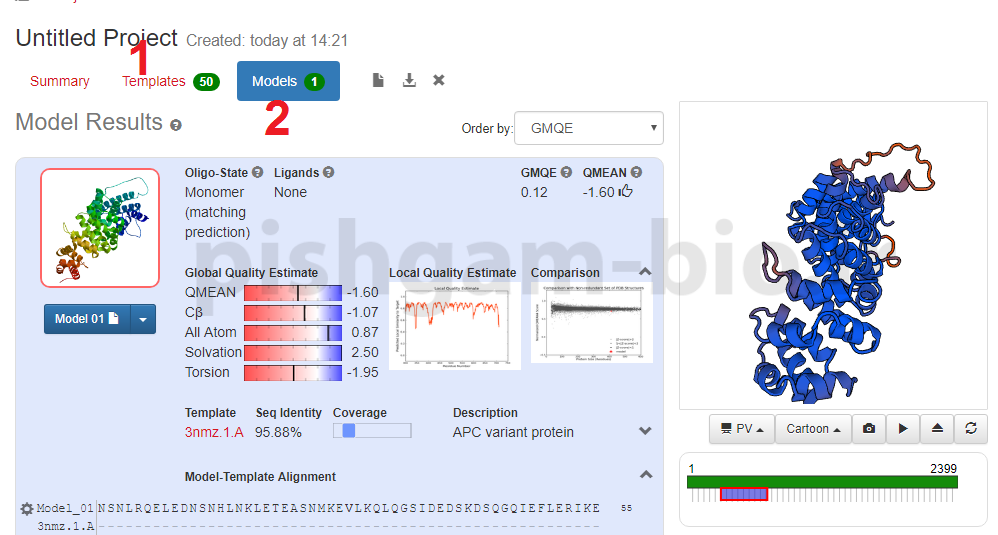
بعد از پیشبینی ساختار سهبعدی نتیجه آن در صفحه فوق نمایش داده می شود.
1: در قسمت Template میتوانید الگوهایی که برای پیشبینی ساختار سهبعدی انتخاب شده اند را مشاهده و الگوهای دلخواه را مشاهده نمایید.
2: قسمت Model میتوانید مدل های ساختار سهبعدی پروتئین که پیشبینی شده اند را مشاهده نماییدکه در این شکل فقط یک مدل ارائه شده است.
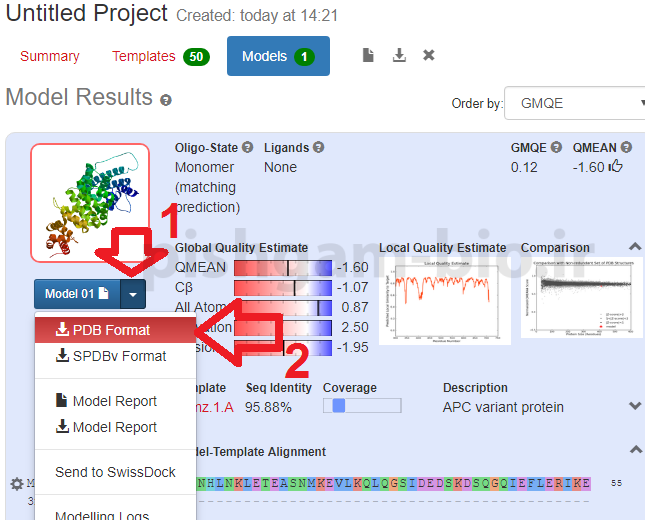
برای دانلود فایل PDB مدل اراده شده مانند شکل فوق بر روی عبارت PDB format کلیک نمایید.
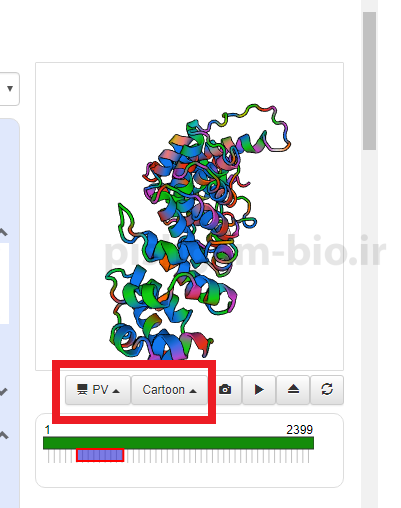
در این قسمت نیز ساختار سهبعدی پروتئین نمایش داده می شود که با استفاده از دو گزینه فوق میتوانید نحوه نمایش ساختار را مشاهده نمایید.
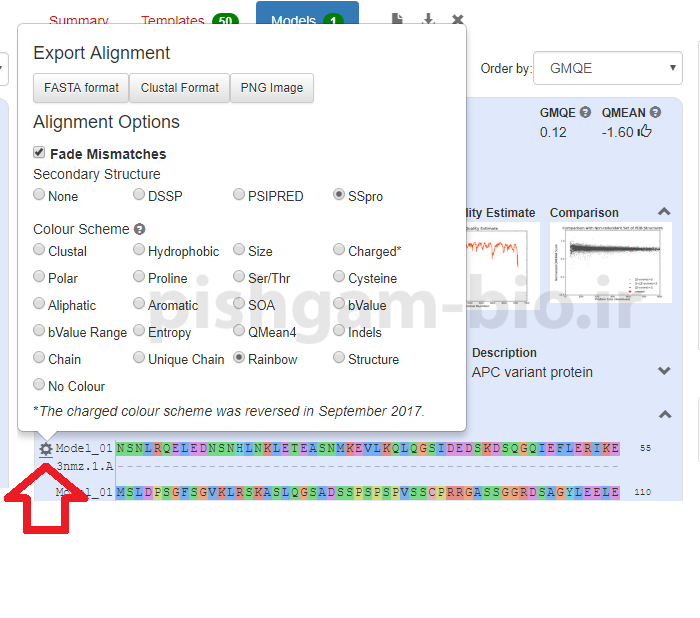
همچنین با کلیک بر روی قسمت فوق میتوانید رنگبندی مدل ارائه شده را تعیین نمایید.
روش دوم: پیش ساختار سهبعدی پروتئینها بر اساس یک ساختار الگو در سایت swissmodel
در این روش ابتدا باید یک فایل PDB از ساختار سهبعدی پروتئین الگو تهیه نمایید و سپس بر اساس ساختار پروتئین الگو ساختار سهبعدی پروتئین مورد نظر خود را پیشبینی نماییم
در صورتی که فایل PDB در اختیار نداشته باشید میتوانید با استفاده از بلاست پروتئین این فایل را تهیه نمود. برای این کار ابتدا بر روی این لینک کلیک نمایید تا به سایت NCBI جهت بلاست پروتئین وارد شوید.
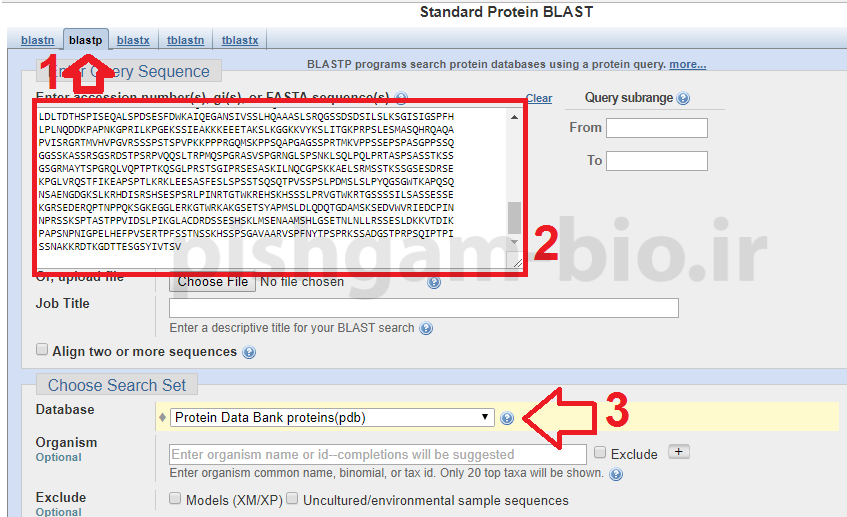
در نرم افزار بلاست
1:ابتدا بر روی زبانه blastp کلیک نمایید
2: توالی پروتئین مربوطه را وارد نمایید
3: در قسمت Database گزینه protein Data Bank proteins(PDB) را انتخاب نمایید.
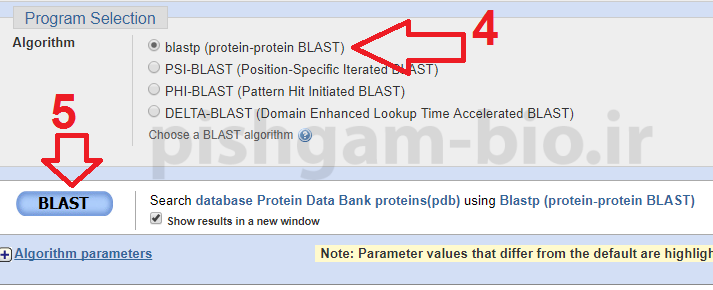
4: این گزینه را انتخاب نمایید
5: بر روی گزینه Blast کلیک نمایید
با مشاهده پنجره فوق باید مدتی صبر نمایید تا فرایند بررسی توالی ویافتن توالی های مشابه انجام شود.
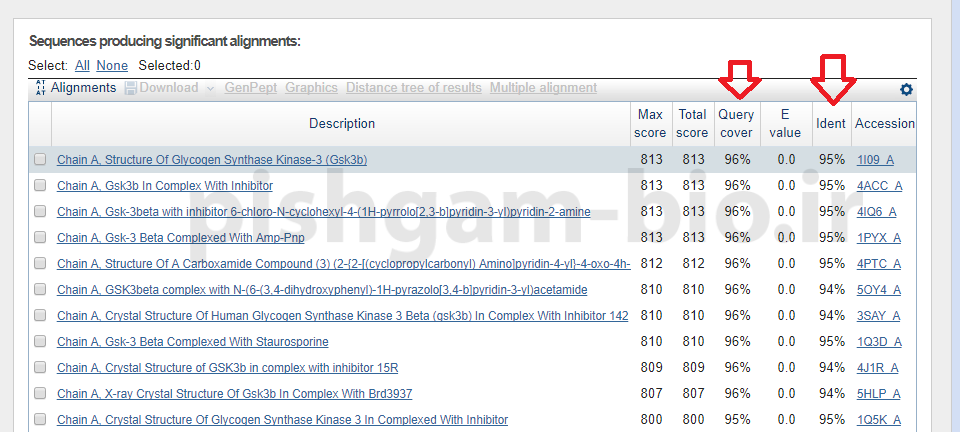
بعد از تکمیل فرایند بررسی توالی در شکل فوق نتایج بلاست را مشاهده مینمایید. همانگونه که مشاهده مینمایید برای توالی وارد شده چندین پروتئین با ساختار مشابه پیشنهاد شده است. بهترین ساختار الگو برای پیشبینی ساختار سهبعدی توالی وارد شده، پروتئینی است که دارای بیشترین میزان identity و Query coverage باشد.
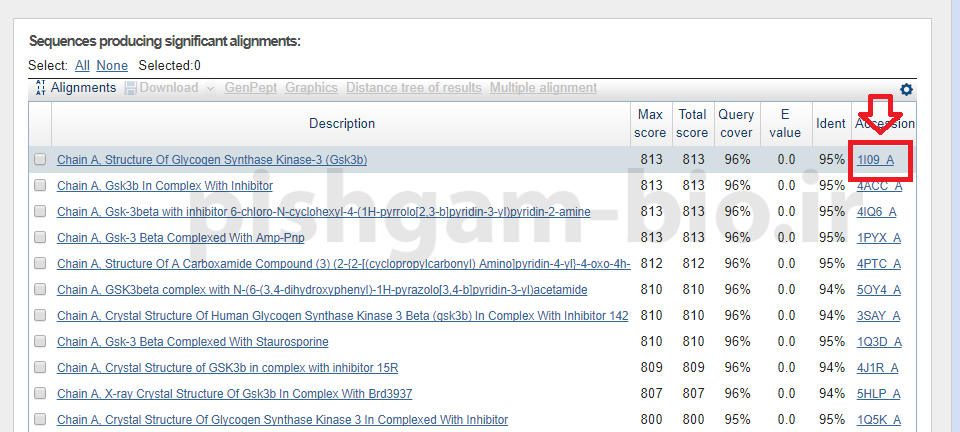
بعد از انتخاب پروتئین مناسب که معمولا اولین گزینه نیز میباشد بر روی Accession آن پروتئین کلیک نمایید تا به صفحه زیر وارد شوید

در صفحه فوق که بیانگر مشخصات پروتئین انتخاب شده میباشد بر روی تصویر مشخص شده کلیک نمایید تا صفحه زیر باز شود.
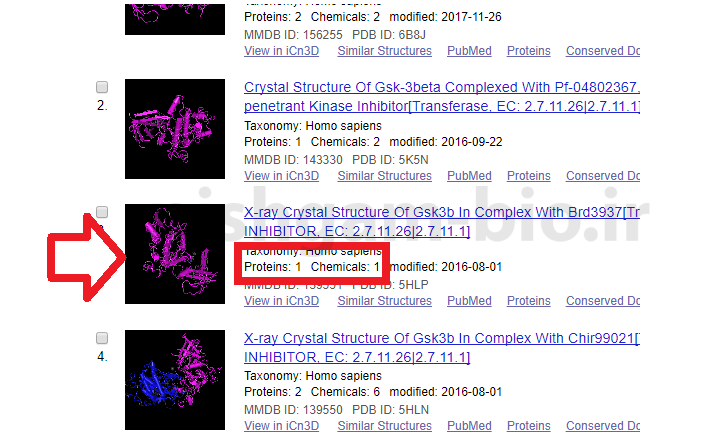
صفحه فوق نشان دهنده ساختارهای سهبعدی برای پروتئین انتخاب شده میباشد از آنجایی که برای یک پروتئین ممکن است به چندین روش ساختار سهبعدی بررسی شده باشد در صفحه فوق چندین ساختار سهبعدی ارائه شده است.
در صفحه فوق ساختاری را انتخاب نمایید که دارای یک protein و دارای کمترین تعداد Chemical باشد سپس بر روی تصویر آن ساختار کلیک نمایید.

سپس در صفحه بعدی بر روی گزینه Download کلیک نمایید تا فایل PDB برای ساختار سهبعدی پروتئین دانلود شود.
سپس ازاین فایل PDB دانلود شده برای پیشبینی ساختار سهبعدی پروتئین دلخواه استفاده مینماییم.
بعد از تهیه فایل PDB و استفاده از آن به عنوان الگو میتوان ساختار سهبعدی پروتئین مورد نظر را پیشبینی نمود برای این کار بر روی لینک زیر کلیک نمایید
https://swissmodel.expasy.org/interactive#structure
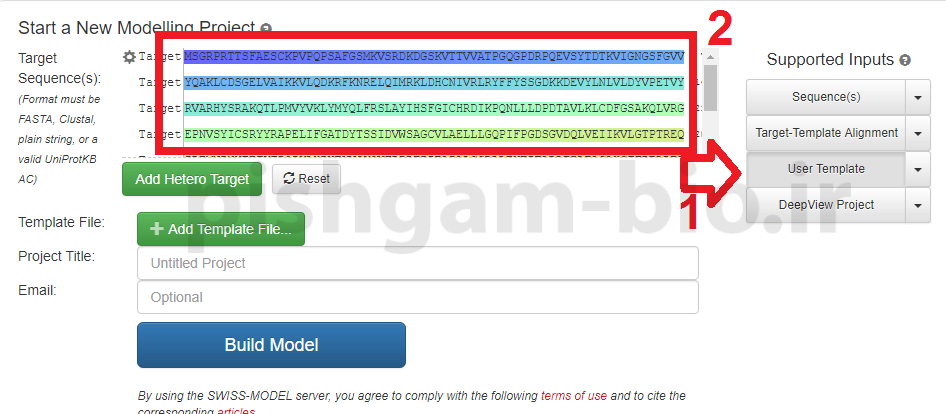
سپس در صفحه فوق:
1: بر روی گزینه User Template کلیک نمایید
2: توالی پروتئینی را وارد نمایید
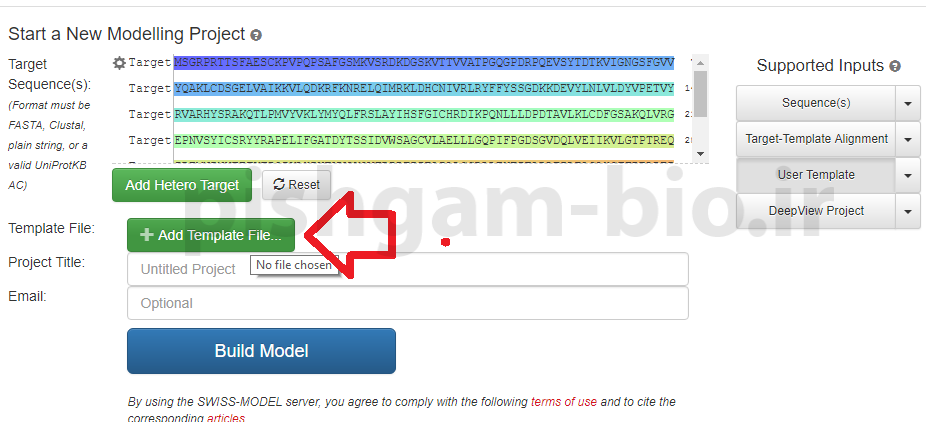
سپس باید توالی الگو را وارد نمایید برای این کار بر روی گزینه Add Template file.. کلیک نمایید تا پنجره زیر باز شود.
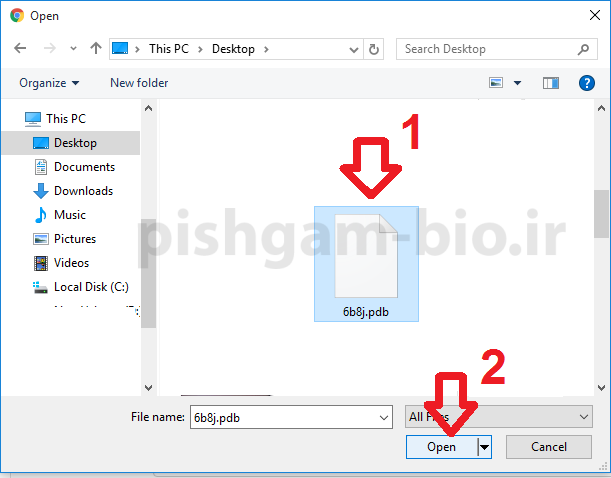
در پنجره فوق فایل الگویی که در مرحله قبل دانلود نمودیم انتخاب نمایید.
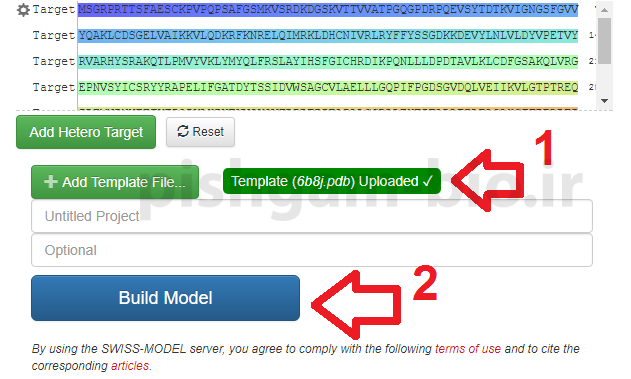
بعد از اینکه فایل الگو دانلود شد بر روی گزینه Build Model کلیک نمایید تا پیشبینی ساختار سهبعدی پروتئین آغاز شود.
سایر مراحل این روش و ارائه نتایج همانگونه میباشد که قبلا ارائه شد.

















4 پاسخ
سلام و وقت بخیر
من یک سوال داشتم وقتی توالی
آمینواسیدی مورد نظرمو وارد سایت SWISSPROT میکنم هیچ مدلی نمیده و این پیغام رو میده:
No templates of sufficient quality to build a homology model were found for your target sequence.
However, 15 templates of low quality were found, you can see them in HTML or text format.
تو سایت NCBI هم وقتی میخوام بلاست کنم این پیغام رو میده: No significant similarity found.
امکانش هست منو راهنمایی کنید باید چیکار کنم. پروتئین مورد نظر من 189 اسید آمینه دارد.
سلام وقتتون بخیر
باید از یک پروتیئن الگو که در توالی دارای شباهت بیشتری با توالی مورد نظرتون هست استفاده کنید
سلام . من ساختار یک پروتئین سطحی یک باکتری (حدودا 190 اسیدآمینه) رو میخوام براساس این روش پیدا کنم ، چون با این روش مدلی پیدا نشد، اگر من خودم یکی از پروتئین های سطحی همین باکتری با حدود 900 اسیدآمینه رو به عنوان مدل انتخاب کنم با توجه به اینکه هنگام بلاست کردن IDENT 60 درصد و QUERY COVER 19 درصد است، آیا مدلی که به دست میآید قابل اطمینان هست ؟
لطفا کار با نرم افزارهای دیگر مثل مدلر و کایمر تدریس شه